Code
import numpy as np
import matplotlib.pyplot as plt
import sympy as sp
from scipy.optimize import fsolve
from scipy.integrate import solve_ivp, odeint
from IPython.display import display, Markdown, MathGloria Faccanoni
06 mars 2026
import numpy as np
import matplotlib.pyplot as plt
import sympy as sp
from scipy.optimize import fsolve
from scipy.integrate import solve_ivp, odeint
from IPython.display import display, Markdown, MathLe modèle S.Z.R., proposée par Munz, Hudea, Imad et Smith en 2009, est une variation du modèle S.I.R pour modéliser une apocalypse zombie.
À chaque instant on décide de diviser la population en trois catégories (qu’on appelle « compartiments » dans le langage de l’épidémiologie): - les individus « Susceptibles » ou « Sains » (S) : ceux qui n’ont jamais eu la maladie et peuvent la contracter ; - les individus « Zombies » (Z) ; - les individus « Rétablis » (R, comme « Recovered » en anglais) : les personnes décédées qui ont la faculté de revenir à la vie (terme \(\zeta R\)) mais aussi les individus débarassés de leur infection (suite à un coup de hache bien placé).
On travaillera avec des variables normalisées : leur valeur est comprise entre \(0\) et \(1\) et représente une fraction de la population totale.
Le modèle s’écrit \( \begin{cases} S'(t)=-\beta S(t)Z(t)\\ Z'(t)=\beta S(t)Z(t)+\zeta R(t)-\alpha S(t) Z(t)\\ R'(t)=\alpha S(t)Z(t)-\zeta R(t) \end{cases} \)
odeint du module scipy.Testons ce modèle avec les coefficients
Dans la suite, considérons les données initiales :
On simulera pour \(t\in[0;60]\) jours.
alpha = 1
beta = 0.5
zeta = 0.25
# yy=[S,I,R]
phi0 = lambda S,Z,R,t : -beta*S*Z
phi1 = lambda S,Z,R,t : (beta-alpha)*S*Z+zeta*R
phi2 = lambda S,Z,R,t : alpha*S*Z-zeta*R
S0 = 0.95
Z0 = 1-S0
R0 = 0
tt = np.linspace(0,60,61) # en jours
h = tt[1]-tt[0]\(P'(t)=S'(t)+Z'(t)+R'(t)=-\beta S(t)Z(t)+\beta S(t)Z(t)+\zeta R(t)-\alpha S(t) Z(t)+\alpha S(t)Z(t)-\zeta R(t)=0\).
On notera \(S_n\approx S(t_n)\), \(Z_n\approx Z(t_n)\) et \(R_n\approx R(t_n)\).
Euler explicite \( \begin{cases} S_{n+1}=S_n+h\varphi_0(S_n,Z_n,R_n,t_n),\\ Z_{n+1}=Z_n+h\varphi_1(S_n,Z_n,R_n,t_n),\\ R_{n+1}=R_n+h\varphi_2(S_n,Z_n,R_n,t_n). \end{cases} \)
# S0, Z0, R0, h variables globales
def euler_progressif(phi0,phi1,phi2,tt):
SS = [S0]
ZZ = [Z0]
RR = [R0]
for i in range(len(tt)-1):
SS.append(SS[i]+h*phi0(SS[i],ZZ[i],RR[i],tt[i]))
ZZ.append(ZZ[i]+h*phi1(SS[i],ZZ[i],RR[i],tt[i]))
RR.append(RR[i]+h*phi2(SS[i],ZZ[i],RR[i],tt[i]))
return [SS,ZZ,RR]
[SS_ep, ZZ_ep, RR_ep] = euler_progressif(phi0,phi1,phi2,tt)
plt.figure(figsize=(10,5))
PP_ep = [SS_ep[i]+ZZ_ep[i]+RR_ep[i] for i in range(len(tt))]
plt.plot(tt,SS_ep,'--',tt,ZZ_ep,'.-',tt,RR_ep,':',tt,PP_ep)
plt.xlabel('t')
plt.legend(['S(t)','Z(t)','R(t)','P(t)'])
plt.title('Euler progressif')
plt.grid()
plt.axis([0,60,0,1.1]);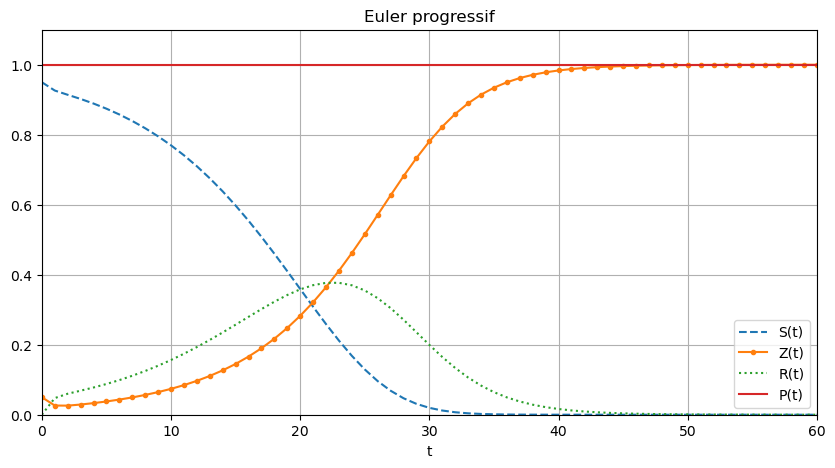
Euler implicite \( \begin{cases} S_{n+1}=S_n+h\varphi_0(S_{n+1},Z_{n+1},R_{n+1},t_{n+1}),\\ Z_{n+1}=Z_n+h\varphi_2(S_{n+1},Z_{n+1},R_{n+1},t_{n+1}),\\ R_{n+1}=R_n+h\varphi_3(S_{n+1},Z_{n+1},R_{n+1},t_{n+1}). \end{cases} \)
# S0, Z0, R0, h variables globales
def euler_regressif(phi0,phi1,phi2,tt):
SS = [S0]
ZZ = [Z0]
RR = [R0]
for i in range(len(tt)-1):
sys = lambda z : [-z[0]+SS[i]+h*phi0(z[0],z[1],z[2],tt[i+1]) ,
-z[1]+ZZ[i]+h*phi1(z[0],z[1],z[2],tt[i+1]) ,
-z[2]+RR[i]+h*phi2(z[0],z[1],z[2],tt[i+1]) ]
Stemp,Ztemp,Rtemp = fsolve( sys , (SS[i],ZZ[i],RR[i]) )
SS.append(Stemp)
ZZ.append(Ztemp)
RR.append(Rtemp)
return [SS,ZZ,RR]
[SS_er, ZZ_er, RR_er] = euler_regressif(phi0,phi1,phi2,tt)
plt.figure(figsize=(10,5))
PP_er=[SS_er[i]+ZZ_er[i]+RR_er[i] for i in range(len(tt))]
plt.plot(tt,SS_er,'--',tt,ZZ_er,'.-',tt,RR_er,':',tt,PP_er)
plt.xlabel('t')
plt.legend(['S(t)','Z(t)','R(t)','P(t)'])
plt.title('Euler regressif')
plt.grid()
plt.axis([tt[0],tt[-1],0,1.1]);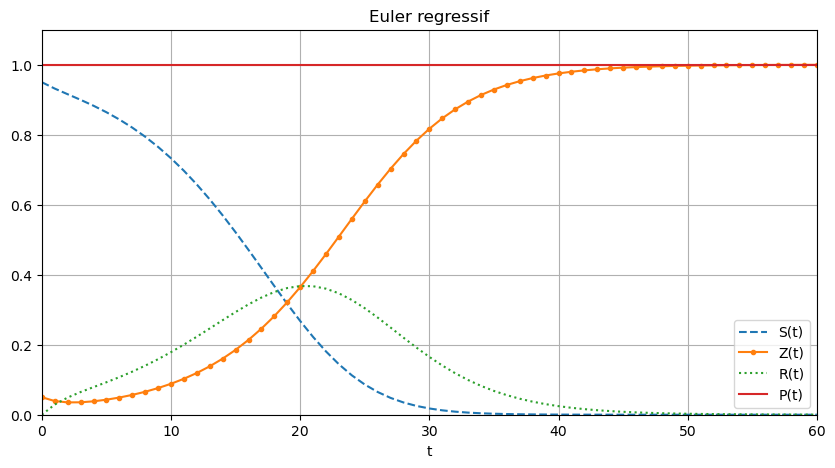
odeint
pphi = lambda yy,t : [ phi0(yy[0],yy[1],yy[2],t), phi1(yy[0],yy[1],yy[2],t), phi2(yy[0],yy[1],yy[2],t) ]
CI = [S0,Z0,R0]
sol = odeint(pphi,CI,tt)
SS,ZZ,RR = sol[:,0],sol[:,1],sol[:,2]
plt.figure(figsize=(10,5))
PP = [SS[i]+ZZ[i]+RR[i] for i in range(len(tt))]
plt.plot(tt,SS,'--',tt,ZZ,'.-',tt,RR,':',tt,PP)
plt.xlabel('t')
plt.legend(['S(t)','Z(t)','R(t)','P(t)'])
plt.title('Odeint')
plt.grid()
plt.axis([0,60,0,1.1]);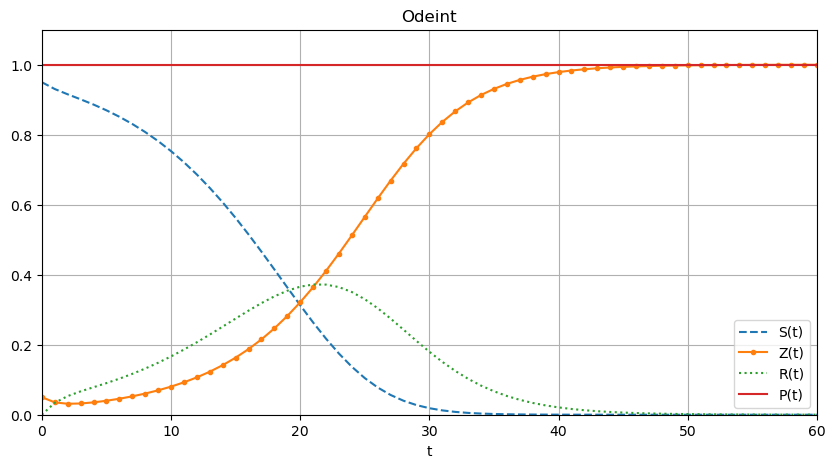
Le modèle S.I.R. a été présenté pour la première fois par KERMACK & McKENDRICK à Londres et Cambridge en 1927 pour expliquer a posteriori l’évolution de l’épidémie de peste à Bombay en 1905-1906.
À chaque instant on décide de diviser la population en trois catégories (qu’on appelle « compartiments » dans le langage de l’épidémiologie): - les individus « Susceptibles » ou « Sains » (S) : ceux qui n’ont jamais eu la maladie et peuvent la contracter ; - les individus « Infectés » (I) : les malades, ce sont aussi les contagieux (c’est une hypothèse de ce modèle) ; - les individus « Rétablis » (R, comme « Recovered » en anglais) : ceux qui ont déjà eu la maladie et sont désormais immunisés contre cette maladie. Dans ce modèle on inclut dans ce groupe les personnes décédées (puisqu’elles ne peuvent plus contracter la maladie).
On travaillera avec des variables normalisées : leur valeur est comprise entre \(0\) et \(1\) et représente une fraction de la population totale (P).
Le modèle s’écrit \( \begin{cases} S'(t)=-\beta S(t)I(t)\\ I'(t)=\beta S(t)I(t)-\nu I(t)\\ R'(t)=\nu I(t) \end{cases} \)
odeint du module scipy.Dans la suite, considérons les données initiales :
Pour la rougeole on prendra
On simulera pour \(t\in[0;90]\) jours.
beta = 0.8
nu = 0.05
# yy=[S,I,R]
phi0 = lambda S,I,R,t : -beta*S*I
phi1 = lambda S,I,R,t : beta*S*I-nu*I
phi2 = lambda S,I,R,t : nu*I
S0=0.99
I0=1-S0
R0=0
tt = np.linspace(0,90,91) # en jours
h = tt[1]-tt[0]\(P'(t)=S'(t)+I'(t)+R'(t)=-\beta S(t)I(t)+\beta S(t)I(t)-\nu I(t)+\nu I(t)=0\).
On notera \(S_n\approx S(t_n)\), \(I_n\approx I(t_n)\) et \(R_n\approx R(t_n)\).
Euler explicite \( \begin{cases} S_{n+1}=S_n+h\varphi_0(S_n,I_n,R_n,t_n),\\ I_{n+1}=I_n+h\varphi_1(S_n,I_n,R_n,t_n),\\ R_{n+1}=R_n+h\varphi_2(S_n,I_n,R_n,t_n). \end{cases} \)
# S0, I0, R0, h variables globales
def euler_progressif(phi0,phi1,phi2,tt):
SS = [S0]
II = [I0]
RR = [R0]
for i in range(len(tt)-1):
SS.append(SS[i]+h*phi0(SS[i],II[i],RR[i],tt[i]))
II.append(II[i]+h*phi1(SS[i],II[i],RR[i],tt[i]))
RR.append(RR[i]+h*phi2(SS[i],II[i],RR[i],tt[i]))
return [SS,II,RR]
[SS_ep, II_ep, RR_ep] = euler_progressif(phi0,phi1,phi2,tt)
plt.figure(figsize=(10,5))
PP_ep=[SS_ep[i]+II_ep[i]+RR_ep[i] for i in range(len(tt))]
plt.plot(tt,SS_ep,'--',tt,II_ep,'.-',tt,RR_ep,':',tt,PP_ep)
plt.xlabel('t')
plt.legend(['S(t)','I(t)','R(t)','P(t)'])
plt.title('Euler progressif')
plt.grid()
plt.axis([tt[0],tt[-1],0,1.1]);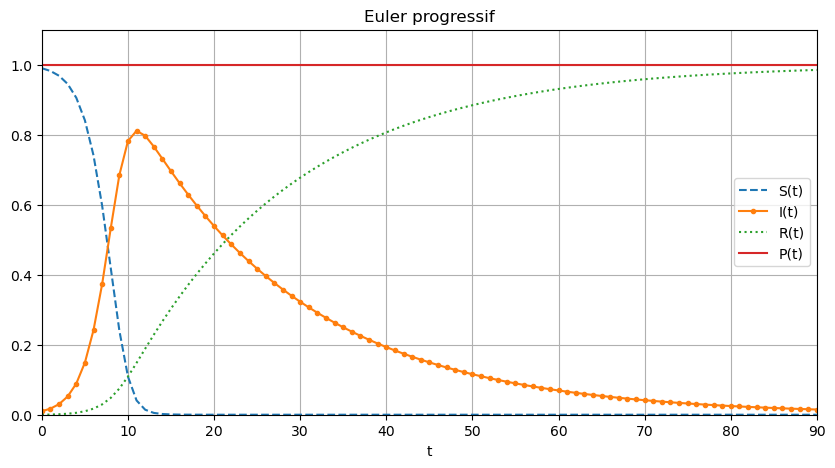
Euler implicite \( \begin{cases} S_{n+1}=S_n+h\varphi_0(S_{n+1},I_{n+1},R_{n+1},t_{n+1}),\\ I_{n+1}=I_n+h\varphi_1(S_{n+1},I_{n+1},R_{n+1},t_{n+1}),\\ R_{n+1}=R_n+h\varphi_2(S_{n+1},I_{n+1},R_{n+1},t_{n+1}). \end{cases} \)
from scipy.optimize import fsolve
# S0, I0, R0, h variables globales
def euler_regressif(phi0,phi1,phi2,tt):
SS = [S0]
II = [I0]
RR = [R0]
for i in range(len(tt)-1):
sys = lambda z : [ -z[0]+SS[i]+h*phi0(z[0],z[1],z[2],tt[i+1]) , -z[1]+II[i]+h*phi1(z[0],z[1],z[2],tt[i+1]) , -z[2]+RR[i]+h*phi2(z[0],z[1],z[2],tt[i+1]) ]
Stemp,Itemp, Rtemp = fsolve( sys , (SS[i],II[i],RR[i]) )
SS.append(Stemp)
II.append(Itemp)
RR.append(Rtemp)
return [SS,II,RR]
[SS_er, II_er, RR_er] = euler_regressif(phi0,phi1,phi2,tt)
plt.figure(figsize=(10,5))
PP_er=[SS_er[i]+II_er[i]+RR_er[i] for i in range(len(tt))]
plt.plot(tt,SS_er,'--',tt,II_er,'.-',tt,RR_er,':',tt,PP_er)
plt.xlabel('t')
plt.legend(['S(t)','I(t)','R(t)','P(t)'])
plt.title('Euler regressif')
plt.grid()
plt.axis([tt[0],tt[-1],0,1.1]);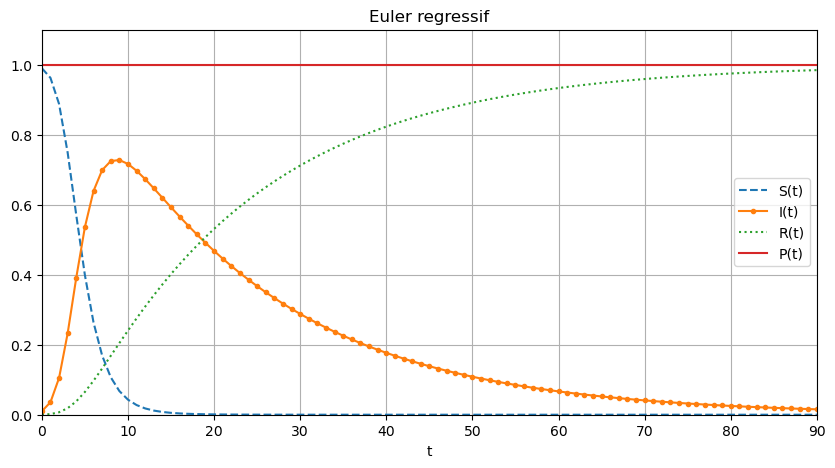
odeint
pphi = lambda yy,t : [ phi0(yy[0],yy[1],yy[2],t), phi1(yy[0],yy[1],yy[2],t), phi2(yy[0],yy[1],yy[2],t) ]
CI = [S0,I0,R0]
sol = odeint(pphi,CI,tt)
SS,II,RR = sol[:,0],sol[:,1],sol[:,2]
plt.figure(figsize=(10,5))
PP = [SS[i]+II[i]+RR[i] for i in range(len(tt))]
plt.plot(tt,SS,'--',tt,II,'.-',tt,RR,':',tt,PP)
plt.xlabel('t')
plt.legend(['S(t)','I(t)','R(t)','P(t)'])
plt.title('Odeint')
plt.grid()
plt.axis([tt[0],tt[-1],0,1.1]);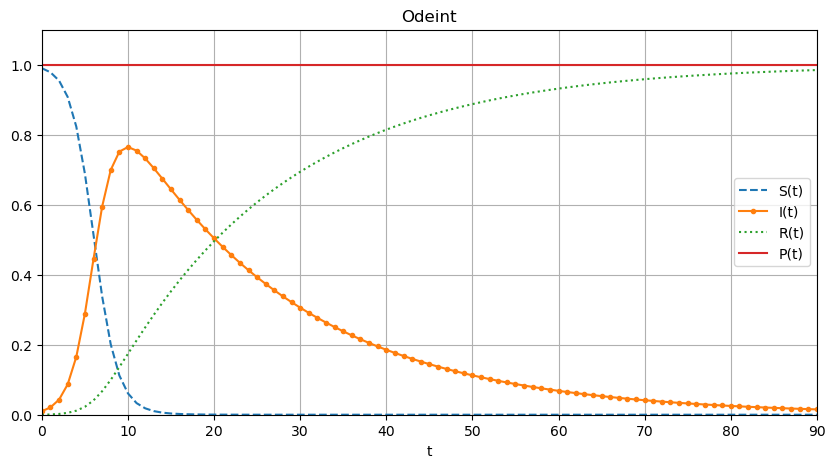
On notera \(\varphi_k\stackrel{\text{déf}}{=}\varphi(t_k,u_k)\). Soit la méthode multipas \( u_{n+1} =2\gamma u_{n} +\left(1-2\gamma \right)u_{n-1} +h\left(\gamma \varphi_{n+1} +\left(2-3\gamma \right)\varphi_{n}\right). \)
\(p=1\): c’est une méthode à \(q=p+1=2\) : - $a_0=2$ et $a_1=1-2$ - $b_0=2-3$ et \(b_1=0\) - $b_{-1}=$
La méthode est implicite si \(\gamma\neq0\).
La méthode est consistante pour tout \(\gamma\) car \( \begin{cases} \displaystyle\sum_{j=0}^p a_j=a_0+a_1=2\gamma+(1-2\gamma)=1, \\ \displaystyle-\sum_{j=0}^p ja_j+\sum_{j=-1}^p b_j=-\big(0a_0+1a_1\big)+\big(b_{-1}+b_0+b_1\big)=-(1-2\gamma)+(\gamma+2-3\gamma)=1 \end{cases} \)
Vérifions ces calculs ci-dessous :
sp.var('gamma')
p=1
a0=2*gamma
a1=1-2*gamma
b0=2-3*gamma
b1=0
bm1=gamma
cond11=a0+a1
cond12=-(0*a0+1*a1)+(bm1+b0+b1)
display(cond11)
display(cond12.factor())
display(sp.solve([sp.Eq(cond11,1),sp.Eq(cond12,1)],gamma))\(\displaystyle 1\)
\(\displaystyle 1\)
[]Le premier polynôme caractéristique est \( \varrho(r)=r^{p+1}-\sum_{j=0}^p a_jr^{p-j}=r^2-a_0r-a_1 {}= r^2-2\gamma r+(2\gamma-1) \) dont les racines sont \( r_0=1,\quad r_1=2\gamma-1. \)
sp.var('r')
rho=r**2-a0*r-a1
display(sp.factor(rho))
sol=sp.solve(rho,r)
display(sol)\(\displaystyle \left(r - 1\right) \left(- 2 \gamma + r + 1\right)\)
[1, 2*gamma - 1]La méthode est zéro-stable ssi \( \begin{cases} |r_j|\le1 \quad\text{pour tout }j=0,\dots,p \\ \varrho'(r_j)\neq0 \text{ si } |r_j|=1, \end{cases} \) donc ssi \(0\le\gamma<1\).
cond=sp.solve([abs(c)<=1 for c in sol],gamma)
print('La première condition impose')
display(cond) La première condition impose\(\displaystyle 0 \leq \gamma \wedge \gamma \leq 1\)
Conclusion : la méthode est convergente ssi elle est consistante et zéro-stable donc ssi \(0\le\gamma<1\).
La méthode est d’ordre au moins 2 car \( \sum_{j=0}^p (-j)^{2}a_j+2\sum_{j=-1}^p (-j)^{1}b_j {}= \big(0^2a_0+1^2a_1\big)+2\big(-(-1)b_{-1}+0b_0+1b_1\big) {}= \big(1-2\gamma\big)+2\big(\gamma\big) {}= 1 \)
cond2=(0*a0+1*a1)+2*(-(-1)*bm1+0*b0+1*b1)
display(cond2.factor())
display(sp.solve(sp.Eq(cond2,1),gamma))\(\displaystyle 1\)
[]La méthode est d’ordre 3 ssi \(\gamma=\frac{2}{5}\) car \( \sum_{j=0}^p (-j)^{3}a_j+3\sum_{j=-1}^p (-j)^{2}b_j {}=-a_1+3\big(b_{-1}+b_1\big) {}=-(1-2\gamma)+3\big(\gamma\big) {}=5\gamma-1=1 \iff \gamma=\frac{2}{5} \)
cond3=(0*a0-1*a1)+3*(1*bm1+0*b0+1*b1)
display(cond3.factor())
display(sp.solve(sp.Eq(cond3,1),gamma))\(\displaystyle 5 \gamma - 1\)
[2/5]Conclusion
On définit la solution exacte (calculée en utilisant le module sympy) pour estimer les erreurs :
# variables globales
t0 = 0
tfinal = 1
y0 = 2
phi = lambda t,y : y*(1-y)
t = sp.Symbol('t')
y = sp.Function('y')
edo = sp.Eq( sp.diff(y(t),t) , phi(t,y(t)) )
solpar = sp.dsolve(edo,y(t),ics={y(t0):y0})
display(Markdown(f'La solution exacte est : \){sp.latex(solpar)}\('))
sol_exacte = sp.lambdify(t,solpar.rhs,'numpy')La solution exacte est : \(y{\left(t \right)} = \frac{1}{1 - \frac{e^{- t}}{2}}\)
On calcule la solution approchée pour différentes valeurs de \(N\):
def multipas(phi, tt, gamma):
h = tt[1] - tt[0]
uu = [y0]
uu.append(sol_exacte(tt[1]))
for i in range(1,len(tt) - 1):
temp = fsolve( lambda x : -x+2*gamma*uu[i]+(1-2*gamma)*uu[i-1]+h*(gamma*phi(tt[i+1],x)+(2-3*gamma)*phi(tt[i],uu[i])) ,uu[i])
uu.append( temp[0] )
return uu
H = np.array([])
err_mp_2 = np.array([])
err_mp_3 = np.array([])
N = 10
for k in range(7):
N += 20
tt = np.linspace(t0, tfinal, N + 1)
h = tt[1] - tt[0]
yy = sol_exacte(tt)
uu_mp_2 = multipas(phi, tt, 1/5)
uu_mp_3 = multipas(phi, tt, 2/5)
H = np.append(H,h)
err_mp_2 = np.append(err_mp_2,np.linalg.norm(uu_mp_2-yy,np.inf))
err_mp_3 = np.append(err_mp_3,np.linalg.norm(uu_mp_3-yy,np.inf))
ordre_mp_2 = np.polyfit(np.log(H),np.log(err_mp_2), 1)[0]
ordre_mp_3 = np.polyfit(np.log(H),np.log(err_mp_3), 1)[0]
print ('Multipas gamma=1/5 ordre=%1.2f' %(ordre_mp_2))
print ('Multipas gamma=2/5 ordre=%1.2f' %(ordre_mp_3))
plt.figure(figsize=(8,5))
plt.plot(np.log(H), np.log(err_mp_2), 'r-o', label=r'MPL avec $\gamma=\frac{1}{5}$')
plt.plot(np.log(H), np.log(err_mp_3), 'b-o', label=r'MPL avec $\gamma=\frac{2}{5}$')
plt.xlabel(r'$\ln(h)$')
plt.ylabel(r'$\ln(e)$')
plt.legend(bbox_to_anchor=(1.04, 1), loc='upper left')
plt.grid(True)
plt.show()
Multipas gamma=1/5 ordre=1.97
Multipas gamma=2/5 ordre=2.94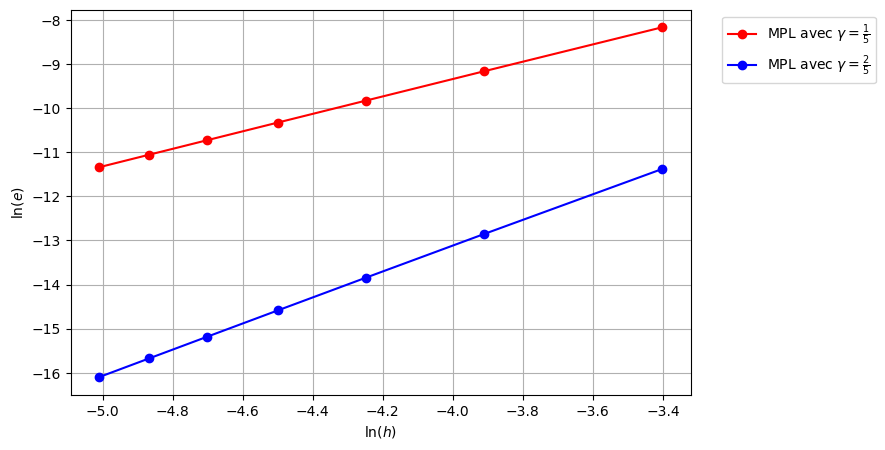
On notera \(\varphi_k\stackrel{\text{déf}}{=}\varphi(t_k,u_k)\). Soit la méthode multipas \( u_{n+1} =2(1-\gamma) u_{n} +\left(2\gamma-1 \right)u_{n-1} +h(1-\gamma) \varphi_{n+1} +h\left(3\gamma-1\right)\varphi_{n}. \)
\(p=1\): c’est une méthode à \(q=p+1=2\) : - $a_0=2(1-) $ et \(a_1=2\gamma-1\) - $b_0=3 $ et \(b_1=0\) - $b_{-1}=1-$
La méthode est implicite si \(\gamma\neq1\).
La méthode est consistante pour tout \(\gamma\) car \( \begin{cases} \displaystyle\sum_{j=0}^p a_j=a_0+a_1=2(1-\gamma) +(2\gamma-1)=1, \\ \displaystyle-\sum_{j=0}^p ja_j+\sum_{j=-1}^p b_j=-\big(0a_0+1a_1\big)+\big(b_{-1}+b_0+b_1\big)=-(2\gamma-1)+(1-\gamma+3\gamma-1)=1 \end{cases} \)
Vérifions ces calculs ci-dessous :
sp.var('gamma')
p=1
a0=2*(1-gamma)
a1=2*gamma-1
b0=3*gamma-1
b1=0
bm1=1-gamma
cond11=a0+a1
cond12=-(0*a0+1*a1)+(bm1+b0+b1)
display(cond11)
display(cond12.factor())
display(sp.solve([sp.Eq(cond11,1),sp.Eq(cond12,1)],gamma))\(\displaystyle 1\)
\(\displaystyle 1\)
[]Le premier polynôme caractéristique est \( \varrho(r)=r^{p+1}-\sum_{j=0}^p a_jr^{p-j}=r^2-a_0r-a_1 {}= r^2-2(1-\gamma) r-(2\gamma-1) \) dont les racines sont \( r_0=1,\quad r_1=1-2\gamma. \)
sp.var('r')
rho=r**2-a0*r-a1
display(sp.factor(rho))
sol=sp.solve(rho,r)
display(sol)\(\displaystyle \left(r - 1\right) \left(2 \gamma + r - 1\right)\)
[1, 1 - 2*gamma]La méthode est zéro-stable ssi \( \begin{cases} |r_j|\le1 \quad\text{pour tout }j=0,\dots,p \\ \varrho'(r_j)\neq0 \text{ si } |r_j|=1, \end{cases} \) donc ssi \(0<\gamma\le1\).
cond=sp.solve([abs(c)<=1 for c in sol],gamma)
display(cond)\(\displaystyle 0 \leq \gamma \wedge \gamma \leq 1\)
Conclusion : la méthode est convergente ssi elle est consistante et zéro-stable donc ssi \(0<\gamma\le1\).
La méthode est d’ordre au moins 2 car \( \sum_{j=0}^p (-j)^{2}a_j+2\sum_{j=-1}^p (-j)^{1}b_j {}=\big(0^2a_0+1^2a_1\big)+2\big(-(-1)b_{-1}+0b_0+1b_1\big) {}=\big(2\gamma-1\big)+2\big(1-\gamma\big)=1 \)
cond2=(0*a0+1*a1)+2*(-(-1)*bm1+0*b0+1*b1)
display(cond2.factor())
display(sp.solve(sp.Eq(cond2,1),gamma))\(\displaystyle 1\)
[]La méthode est d’ordre 3 ssi \(\gamma=\frac{2}{5}\) car \( \sum_{j=0}^p (-j)^{3}a_j+3\sum_{j=-1}^p (-j)^{2}b_j=-a_1+3\big(b_{-1}+b_1\big)=-(2\gamma-1)+3\big(1-\gamma\big)=4-5\gamma=1 \iff \gamma=\frac{3}{5} \)
cond3=(0*a0-1*a1)+3*(1*bm1+0*b0+1*b1)
display(cond3.factor())
display(sp.solve(sp.Eq(cond3,1),gamma))\(\displaystyle 4 - 5 \gamma\)
[3/5]Conclusion
On définit la solution exacte (calculée en utilisant le module sympy) pour estimer les erreurs:
# variables globales
t0 = 0
tfinal = 1
y0 = 2
phi = lambda t,y : y*(1-y)
t = sp.Symbol('t')
y = sp.Function('y')
edo= sp.Eq( sp.diff(y(t),t) , phi(t,y(t)) )
solpar = sp.dsolve(edo, y(t), ics={y(t0):y0})
display(Markdown(f'La solution exacte est : \({sp.latex(solpar)}\)'))
sol_exacte = sp.lambdify(t,solpar.rhs,'numpy')La solution exacte est : \(y{\left(t \right)} = \frac{1}{1 - \frac{e^{- t}}{2}}\)
On calcule la solution approchée pour différentes valeurs de \(N\):
def multipas(phi, tt, gamma):
h = tt[1] - tt[0]
uu = np.empty_like(tt)
uu[0] = y0
uu[1] = sol_exacte(tt[1])
for i in range(1,len(tt) - 1):
temp = fsolve( lambda x : -x+2*(1-gamma)*uu[i]+(2*gamma-1)*uu[i-1]+h*(1-gamma)*phi(tt[i+1],x)+h*(3*gamma-1)*phi(tt[i],uu[i]) ,uu[i])
uu[i+1] = temp[0]
return uu
H = np.array([])
err_mp_2 = np.array([])
err_mp_3 = np.array([])
N = 10
for k in range(7):
N += 20
tt = np.linspace(t0, tfinal, N + 1)
h = tt[1] - tt[0]
yy = sol_exacte(tt)
uu_mp_2 = multipas(phi, tt, 1/5)
uu_mp_3 = multipas(phi, tt, 3/5)
H = np.append(H,h)
err_mp_2 = np.append(err_mp_2,np.linalg.norm(uu_mp_2-yy,np.inf))
err_mp_3 = np.append(err_mp_3,np.linalg.norm(uu_mp_3-yy,np.inf))
ordre_mp_2 = np.polyfit(np.log(H),np.log(err_mp_2), 1)[0]
ordre_mp_3 = np.polyfit(np.log(H),np.log(err_mp_3), 1)[0]
print (f'MPL avec gamma=1/5 ordre={ordre_mp_2:.2f}')
print (f'MPL avec gamma=3/5 ordre={ordre_mp_3:.2f}')
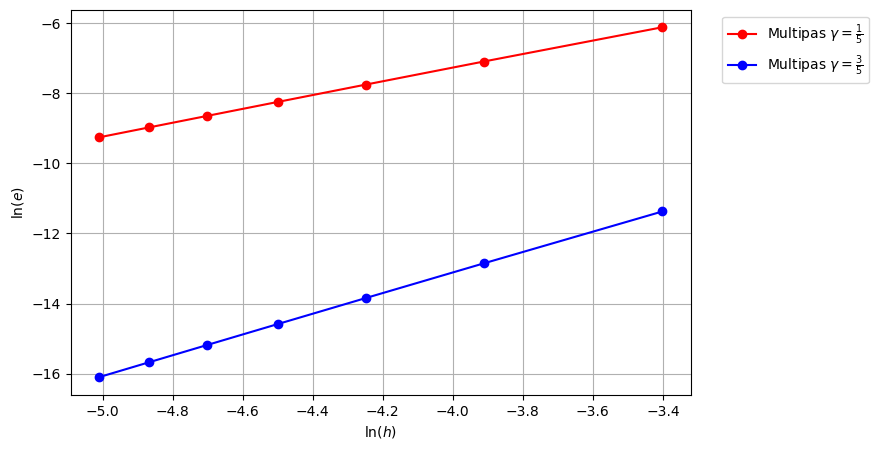
plt.figure(figsize=(8,5))
plt.plot(np.log(H), np.log(err_mp_2), 'r-o', label=r'Multipas $\gamma=\frac{1}{5}$')
plt.plot(np.log(H), np.log(err_mp_3), 'b-o', label=r'Multipas $\gamma=\frac{3}{5}$')
plt.xlabel(r'$\ln(h)$')
plt.ylabel(r'$\ln(e)$')
plt.legend(bbox_to_anchor=(1.04, 1), loc='upper left')
plt.grid(True)
plt.show()
MPL avec gamma=1/5 ordre=1.95
MPL avec gamma=3/5 ordre=2.94